「電子線トモグラフィー」の版間の差分
(→トモグラム画像の解釈) |
|||
| (同じ利用者による、間の153版が非表示) | |||
| 行4: | 行4: | ||
== [[連続傾斜像の撮影]] == | == [[連続傾斜像の撮影]] == | ||
| − | <div> | + | <div> この手法で試料を撮影すると特定の軸に対して一定間隔で傾斜した画像になります。また、傾斜角度が大きくなるにつれて視野は広くなるので、映っている物体は傾斜軸の中心に集まってきます。</div> |
<br> | <br> | ||
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td>[[画像:Input- | + | <td>[[画像:Input-Tomogram1.png]]<br> |
| − | <p align="Center"> | + | <p align="Center">1軸傾斜 (中央が0°の画像)<br></p> |
| − | + | </td> | |
| − | <p align="Center"> | + | </tr> |
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>2軸傾斜の画像を得るときはときは試料を90°回転させて、1軸傾斜と同様の方法で撮影します。</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>[[画像:Input-Tomogram2.png]]<br> | ||
| + | <p align="Center">2軸傾斜(中央が0°の画像)(上の画像より90°回転した向きになっている)<br></p> | ||
</td> | </td> | ||
</tr> | </tr> | ||
| 行25: | 行33: | ||
傾斜画像の中心付近の画像の相関から、それぞれの傾斜画像の大まかな位置を合わせます。 | 傾斜画像の中心付近の画像の相関から、それぞれの傾斜画像の大まかな位置を合わせます。 | ||
| − | <div>[[Media:1WDC- | + | <div>[[Media:1WDC-Tom-2dSet.zip|入力ファイル]](Y軸周りに±60°の範囲で2°刻みで傾斜)<br> |
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-2dSet.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行60: | 行68: | ||
<br> | <br> | ||
| − | <div>[[Media:1WDC- | + | <div>[[Media:1WDC-Tom-mask-2dSet.zip|出力ファイル]](.mask)<br> |
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-mask-2dSet.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行71: | 行79: | ||
===位置合わせ=== | ===位置合わせ=== | ||
| − | + | <div> 傾斜角度に応じて対象が平行移動しているので、位置を合わせます。このとき傾斜による影響を受けにくくするために隣同士の角度で位置合わせを行います。<br> | |
| − | <div> | + | 例. 2°刻みで撮影した画像の場合<br> |
| + | 2°画像の位置を0°画像の位置に合わせる<br> | ||
| + | 4°画像の位置を'''位置補正後の'''2°画像の位置に合わせる<br> | ||
| + | 6°画像の位置を'''位置補正後の'''4°画像の位置に合わせる<br> | ||
| + | .<br> | ||
| + | .<br> | ||
| + | (+が終わったら-についても同様に位置を合わせる)</div> | ||
<br> | <br> | ||
| − | <div>[[Media:1WDC- | + | ====[[mrcImageCorrelation]]を使用した場合==== |
| + | <div> [[Media:Makefile-Tomogram.zip|こちらのMakefile]]を使用して位置合わせを実行します。Makefileを使用せずにコマンドを逐次入力しても位置合わせは可能ですが、[[mrc2Dto3D]]用の入力ファイルリストを作成する必要があります。</div> | ||
| + | <br> | ||
| + | |||
| + | =====実行例1===== | ||
| + | <div>[[Media:1WDC-Tom-mask-2dSet.zip|入力ファイル]]<br> | ||
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-mask-2dSet.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行85: | 行104: | ||
<br> | <br> | ||
| − | <div>[[Media:1WDC- | + | <div>コマンド</div> |
| + | <pre> | ||
| + | make CorFit1 | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:1WDC-Tom-Fit-2d.zip|出力ファイル]](.fit)</div> | ||
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-Fit-2d.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行95: | 行120: | ||
<br> | <br> | ||
| − | <div> | + | == [[ファイン・アラインメント]] == |
| + | <div> 傾斜画像の軸の位置、角度を出来る限り一致させます。</div> | ||
| + | <br> | ||
| + | |||
| + | ===実行例1(傾斜軸の調整)=== | ||
| + | <div> 軸の傾きは[[mrcImageTiltAxisSearch]]で算出することができます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:1WDC-Tom-Tilt-2dSet.zip|入力ファイル]](傾斜軸を10°傾けた1軸傾斜のデータ)<br> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:1WDC-Tom-Tilt-2dSet.png]]<br> | ||
| + | 10°刻みで表示<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Makefile-Tomogram1.zip|使用Makefile]]の設定</div> | ||
<pre> | <pre> | ||
| − | ### | + | # RotMode |
| − | # | + | ROTMODE=ZOYS |
| − | + | # Rot1 | |
| − | # | + | ROT1MIN=10 |
| − | + | ROT1MAX=10 | |
| + | ROT1D=10 | ||
| + | # Rot2 | ||
| + | ROT2MIN=-60 | ||
| + | ROT2MAX=60 | ||
| + | ROT2D=2 | ||
| + | # Rot3 | ||
| + | ROT3MIN=0 | ||
| + | ROT3MAX=0 | ||
| + | ROT3D=30 | ||
| + | ### For mrcImageMove | ||
| + | SHIFT2MAX=10 | ||
| + | SHIFT3MAX=0 | ||
| + | ### For mrcImageTiltAxisSearch | ||
| + | TILTMIN=0 | ||
| + | TILTMAX=20 | ||
| + | TILTN=10 | ||
| + | TILTITER=1 | ||
| + | TILTSCALE=5 | ||
</pre> | </pre> | ||
| + | <br> | ||
<div>コマンド</div> | <div>コマンド</div> | ||
<pre> | <pre> | ||
| − | make | + | make TiltFit |
</pre> | </pre> | ||
<br> | <br> | ||
| − | <div> | + | <div>出力した軸の傾き(.tiltinfoファイルに格納される)</div> |
| − | + | ||
<pre> | <pre> | ||
| − | + | 9.895 | |
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
| − | + | ||
</pre> | </pre> | ||
| − | |||
<br> | <br> | ||
| − | <div>[[Media:1WDC- | + | <div>3次元再構成したときの違い</div> |
| + | <table> | ||
| + | <tr> | ||
| + | <td>補正前</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>[[画像:Outdata-Tomogram4.png]]</td> | ||
| + | <td>[[画像:Outdata1-Tomogram4.png]]</td> | ||
| + | <td>[[画像:Outdata2-Tomogram4.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>補正後</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>[[画像:Outdata-Tomogram5.png]]</td> | ||
| + | <td>[[画像:Outdata1-Tomogram5.png]]</td> | ||
| + | <td>[[画像:Outdata2-Tomogram5.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>yz平面</td> | ||
| + | <td>zx平面</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ===実行例2(傾斜軸の繰り返し調整)=== | ||
| + | <div>出力された軸の傾きを中心として、繰り返し[[mrcImageTiltAxisSearch]]を使用します。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:1WDC-Tom-Tilt1-2dSet.zip|入力ファイル]](傾斜軸を1°傾けた1軸傾斜のデータ)<br> | ||
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-Tilt1-2dSet.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行139: | 行218: | ||
<br> | <br> | ||
| − | + | <div>[[Media:Makefile-Tomogram2.zip|使用Makefile]]の設定</div> | |
| − | + | <pre> | |
| + | # For mrcImageTiltAxisSearch | ||
| + | IN_TILT_EXT=roi | ||
| + | # RotMode | ||
| + | ROTMODE=ZEYR | ||
| + | # Rot1 | ||
| + | ROT1MIN=1 | ||
| + | ROT1MAX=1 | ||
| + | ROT1D=1 | ||
| + | # Rot2 | ||
| + | ROT2MIN=-60 | ||
| + | ROT2MAX=60 | ||
| + | ROT2D=10 | ||
| + | # Rot3 | ||
| + | ROT3MIN=0 | ||
| + | ROT3MAX=0 | ||
| + | ROT3D=10 | ||
| + | ### For mrcImageTiltAxisSearch | ||
| + | TILTMIN=-10 | ||
| + | TILTMAX=10 | ||
| + | TILTN=10 | ||
| + | TILTITER=100 | ||
| + | TILTSCALE=5 | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make TiltFit | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>軸の傾きの遷移</div> | ||
| + | <pre> | ||
| + | 0.084 | ||
| + | 0.161 | ||
| + | 0.230 | ||
| + | 0.294 | ||
| + | 0.345 | ||
| + | |||
| + | -中略- | ||
| + | |||
| + | 0.701 | ||
| + | 0.700 | ||
| + | 0.685 | ||
| + | 0.706 | ||
| + | 0.701 | ||
| + | </pre> | ||
| + | <div>傾斜軸の傾きが1付近に近づきます。</div> | ||
| + | <br> | ||
== [[3次元再構成]] == | == [[3次元再構成]] == | ||
| − | 2次元画像のセットから3次元画像を再構成します。 | + | <div> 2次元画像のセットから3次元画像を再構成します。</div> |
| + | <br> | ||
| + | |||
| + | <div>[[Media:1WDC-shift1.3d|元の3Dデータ]]の画像</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:1WDC-shift1-3d.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:1WDC-shift1-3d2.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:1WDC-shift1-3d3.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">0 (0, 0, 0)<br> | ||
| + | 4 (31, 26, 26)<br> | ||
| + | 0.0116844<br> | ||
| + | 0.147033<br> | ||
| + | 0.000287174<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
<br> | <br> | ||
===[[mrc2Dto3D]]で実行=== | ===[[mrc2Dto3D]]で実行=== | ||
| − | ====実行例1==== | + | ====実行例1(1軸傾斜での再構成)==== |
<div> 連続傾斜像の撮影で軸にズレがない場合は角度刻みをそのまま入力ファイルリストに設定します。</div> | <div> 連続傾斜像の撮影で軸にズレがない場合は角度刻みをそのまま入力ファイルリストに設定します。</div> | ||
<br> | <br> | ||
| − | <div>[[Media:1WDC- | + | <div>[[Media:1WDC-Tom-Fit-2d.zip|入力ファイル]]<br> |
<table> | <table> | ||
<tr> | <tr> | ||
| − | <td><p align="Center">[[画像:1WDC- | + | <td><p align="Center">[[画像:1WDC-Tom-Fit-2d.png]]<br> |
| − | + | 10°刻みで表示<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
</table> | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド: [[mrc2Dto3D]] -i Input.3dlst -o Input.3d -m 1</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Makefile-Tomogram.zip|こちらのMakefile]]を使用すれば、以下のコマンドでも実行できます。</div> | ||
| + | <div>設定内容</div> | ||
| + | <pre> | ||
| + | # For Reconstruction | ||
| + | IN_3D_EXT=fit | ||
| + | # RotMode | ||
| + | ROTMODE=YOYS | ||
| + | # Rot1 | ||
| + | ROT1MIN=-60 | ||
| + | ROT1MAX=60 | ||
| + | ROT1D=2 | ||
| + | # Rot2 | ||
| + | ROT2MIN=0 | ||
| + | ROT2MAX=0 | ||
| + | # Rot3 | ||
| + | ROT3MIN=0 | ||
| + | ROT3MAX=0 | ||
| + | </pre> | ||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make 3DList | ||
| + | make Input.3d | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>出力ファイル(Input.3d)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Outdata-mrc2Dto3D.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata1-mrc2Dto3D.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata2-mrc2Dto3D.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00437076 (39, 34, 36)<br> | ||
| + | 0.00799233 (37, 34, 36)<br> | ||
| + | 3.45089e-06<br> | ||
| + | 0.000342836<br> | ||
| + | 6.69601e-07<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ====実行例2(2軸傾斜での再構成)==== | ||
| + | <div>2軸で傾斜した画像にて3次元再構成を行います。</div> | ||
| + | <div>[[Media:1WDC-Tom1-2dSet.zip|入力ファイル]](X, Y軸周りに±60°の範囲でそれぞれ10°刻みで傾斜)<br> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:1WDC-Tom1-2dSet.png]]<br> | ||
| + | 1行目がX軸傾斜、2行目がY軸傾斜<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Makefile-Tomogram6.zip|こちらのMakefile]]を使って3次元再構成を行います。</div> | ||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make all | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>途中で使用する範囲を決めるために[[Display2]]が起動しますが、今回は全ての範囲を選択してROI情報を保存します。<br> | ||
| + | 今回出力したInformationファイル</div> | ||
| + | <pre> | ||
| + | DataA_006.mrcsmth-0000.roi Rect 0.000000 0.000000 63.000000 0.000000 63.000000 63.000000 0.000000 63.000000 | ||
| + | </pre> | ||
<br> | <br> | ||
| + | |||
| + | <div>出力ファイル</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Outdata-Tomogram2.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata1-Tomogram2.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata2-Tomogram2.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-9.32199 (29, 37, 34)<br> | ||
| + | 21.995 (40, 35, 32)<br> | ||
| + | 0.0280746<br> | ||
| + | 1.38771<br> | ||
| + | 0.00271036<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ====実行例3(Doubleを使用した2軸傾斜での再構成)==== | ||
| + | <div>[[mrc2Dto3D]]のオプション -Doubleを使用して3次元再構成を行います。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>変更箇所</div> | ||
| + | <pre> | ||
| + | .roilst.mrc3d: | ||
| + | # mrc2Dto3D -I $*.roilst -o $*.mrc3d -single 0 -InterpolationMode 2 -m 1 | ||
| + | mrc2Dto3D -I $*.roilst -o $*.mrc3d -Double -InterpolationMode 2 -m 1 | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>出力ファイル</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Outdata-Tomogram6.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata1-Tomogram6.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata2-Tomogram6.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-10360.9 (41, 24, 0)<br> | ||
| + | 8132.05 (40, 35, 31)<br> | ||
| + | 86.0574<br> | ||
| + | 673.594<br> | ||
| + | 1.31561<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ===ラドン変換を使った3次元再構成で実行=== | ||
| + | <div> [[mrc2Dto3D]]を使用するほかにラドン変換から3次元像を作る方法があります。ラドン変換は以下の流れで行います。 | ||
| + | <br> | ||
| + | |||
| + | 位置合わせ済みの2Dリスト<br> | ||
| + | ↓[[mrcImageSinogramCreate]]<br> | ||
| + | シノグラムリスト<br> | ||
| + | ↓[[mrcRadon2Dto3D]]<br> | ||
| + | 3Dラドンファイル<br> | ||
| + | ↓[[mrcImageInverseRadonTransform]]<br> | ||
| + | 3Dファイル(完了)</div> | ||
| + | <br> | ||
| + | |||
| + | ====実行例1==== | ||
| + | <div>[[Media:Makefile-Tomogram7.zip|こちらのMakefile]]を使い、[[Media:1WDC-Tom2-2dSet.zip|実行例2で作成された .roilstファイル]]について実行します。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make Radon3D | ||
| + | </pre> | ||
<div>出力ファイル</div> | <div>出力ファイル</div> | ||
| 行169: | 行497: | ||
</tr> | </tr> | ||
<tr> | <tr> | ||
| − | <td>[[画像:Outdata- | + | <td>[[画像:Outdata-Tomogram3.png]]</td> |
| − | <td>[[画像:Outdata1- | + | <td>[[画像:Outdata1-Tomogram3.png]]</td> |
| − | <td>[[画像:Outdata2- | + | <td>[[画像:Outdata2-Tomogram3.png]]</td> |
| + | </tr> | ||
| + | </table> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">1.84923e+06 (0, 59, 28)<br> | ||
| + | 1.17991e+07 (34, 31, 30)<br> | ||
| + | 3.63631e+06<br> | ||
| + | 1.64358e+06<br> | ||
| + | 3536.42<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ====実行例2==== | ||
| + | <div> [[Media:Makefile-Tomogram7.zip|こちらのMakefile]]から逆ラドン変換のオプションを変更して実行します。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>変更内容</div> | ||
| + | <pre> | ||
| + | ### RadonTransform | ||
| + | RBP_MODE=4 | ||
| + | RBP_OPTION=-Rmin 0.05 -Rmax 0.1 | ||
| + | </pre> | ||
| + | |||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make Radon3D | ||
| + | </pre> | ||
| + | |||
| + | <div>出力ファイル</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>yz平面</td> | ||
| + | <td>zx平面</td> | ||
</tr> | </tr> | ||
<tr> | <tr> | ||
| − | <td>[[画像: | + | <td>[[画像:Outdata-Tomogram7.png]]</td> |
| − | <td>[[画像: | + | <td>[[画像:Outdata1-Tomogram7.png]]</td> |
| − | <td>[[ | + | <td>[[画像:Outdata2-Tomogram7.png]]</td> |
</tr> | </tr> | ||
</table> | </table> | ||
| 行187: | 行557: | ||
標準誤差<br></p> | 標準誤差<br></p> | ||
</td> | </td> | ||
| − | <td><p align="left">- | + | <td><p align="left">-344789 (25, 25, 0)<br> |
| − | + | 631546 (37, 34, 28)<br> | |
| − | + | 4381.1<br> | |
| − | + | 76358.4<br> | |
| − | + | 164.297<br></p> | |
</td> | </td> | ||
</tr> | </tr> | ||
| 行198: | 行568: | ||
== [[電子線トモグラフィー画像のもつ問題点]] == | == [[電子線トモグラフィー画像のもつ問題点]] == | ||
| − | + | ===ミッシングエリア=== | |
| + | <div> 全方位からの投影像を得られないために、ミッシングエリア(1軸の場合はウェッジ、2軸の場合はピラミッド)とよばれる情報がない領域があります。そのため、方向依存でのボケを生じます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[:Media:Makefile-Tomogram5.zip|使用MakeFile]]を使用します。</div> | ||
| + | <div>[[:Media:Input-ellipsoidal.3d|元の3次元像]](Target.ini3dにリネーム)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-ellipsoidal.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-ellipsoidal.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-ellipsoidal.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">0 (0, 0, 0)<br> | ||
| + | 2 (29, 29, 14)<br> | ||
| + | 0.108302<br> | ||
| + | 0.364429<br> | ||
| + | 0.000711774<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>1軸傾斜で投影して3次元再構成した場合(Y軸: -60° ~ 60°: 10°刻み)</div> | ||
| + | <div>変更箇所</div> | ||
| + | <pre> | ||
| + | TILTAXISNUMBER=1 # Single: 1 Double: 2 | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make Target.ini2d | ||
| + | make TestData2DSet | ||
| + | make all | ||
| + | </pre> | ||
| + | <br> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Output-ellipsoidal.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Output1-ellipsoidal.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Output2-ellipsoidal.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00330818 (52, 36, 32)<br> | ||
| + | 0.00425516 (13, 37, 32)<br> | ||
| + | 2.08481e-05<br> | ||
| + | 0.000467848<br> | ||
| + | 9.13766e-07<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div></div> | ||
| + | <br> | ||
| + | |||
| + | <div>2軸傾斜で投影して3次元再構成した場合(X, Y軸: 各-60° ~ 60°: 10°刻み)</div> | ||
| + | <div>変更箇所</div> | ||
| + | <pre> | ||
| + | TILTAXISNUMBER=2 # Single: 1 Double: 2 | ||
| + | </pre> | ||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make Target.ini2d1 | ||
| + | make TestData2DSetDouble | ||
| + | make all | ||
| + | </pre> | ||
| + | <br> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Output3-ellipsoidal.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Output4-ellipsoidal.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Output5-ellipsoidal.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00248567 (12, 38, 32)<br> | ||
| + | 0.00344027 (13, 37, 32)<br> | ||
| + | 2.07529e-05<br> | ||
| + | 0.000401237<br> | ||
| + | 7.83666e-07<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div></div> | ||
| + | <br> | ||
| + | |||
| + | ===画像の位置、フォーカスの問題=== | ||
| + | <div> 試料を傾けながら撮影するため回転軸からの距離に応じてレンズとの距離が変化していきます。これによって生じる問題をいかに補正するかも一つのポイントとなります。</div> | ||
| + | <br> | ||
| + | |||
| + | ====平行移動の補正==== | ||
| + | <div> 傾斜する角度が大きくなるほど、視野が広くなるため試料は傾斜軸の方へ近づいていきます。これを補正するために[[mrcImageCorrelation]]などを使ってどれだけ平行移動が必要かを計算します。また、試料を傾斜する毎に形も変わっていきますので比較はできるだけ近い画像同士で行います。</div> | ||
| + | <br> | ||
| + | |||
| + | ====軸の決定==== | ||
| + | <div> 撮影した画像は必ずしも設定した軸を中心に傾斜しているとは限りません。これは電子顕微鏡自体の性能や試料の設置方法などによって多少のズレが生じてしまうからです。傾斜軸のズレは[[mrcImageTiltAxisSearch]]などを使って計算します。</div> | ||
| + | <br> | ||
== トモグラフに使われる画像処理 == | == トモグラフに使われる画像処理 == | ||
| + | <div> 再構成した3次元画像の解析を行う前処理として以下のような処理を施します。</div> | ||
| + | <br> | ||
| + | |||
=== 平滑化 === | === 平滑化 === | ||
| + | <div> 再構成した3次元像のノイズを除去するため平滑化を行います。</div> | ||
| + | <br> | ||
| + | |||
| + | ====実行例1==== | ||
| + | <div>[[Media:Input-Tomogram3D.mrc|入力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-Tomogram3D.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-Tomogram3D.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-Tomogram3D.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00268221 (76, 92, 66)<br> | ||
| + | 0.00642324 (89, 42, 71)<br> | ||
| + | 2.0386e-06<br> | ||
| + | 0.000254286<br> | ||
| + | 1.63933e-07<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド: [[mrcImageSmoothing]] -i Input-Tomogram3D.mrc -o Input-TomogramSmth.mrc -m 1</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-TomogramSmth.mrc|出力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-TomogramSmth.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-TomogramSmth.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-TomogramSmth.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00136636 (75, 42, 133)<br> | ||
| + | 0.00292404 (94, 65, 68)<br> | ||
| + | -9.48921e-07<br> | ||
| + | 0.00013513<br> | ||
| + | 8.71152e-08<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
=== セグメンテーション === | === セグメンテーション === | ||
| + | トモグラムは多様な構造を含むため、3次元画像から興味あるセグメントを切り出すなどの作業が必要です。そのための支援ソフトウェアが必要です。場合によっては2次元画像から切り出すこともあります。<br> | ||
| + | <br> | ||
| − | == | + | ====3次元画像の切り出し==== |
| − | + | <div> 再構成された3次元画像から粒子と考えられる部分などを切り出します。切り出したデータは3次元画像の解析や平均化するときに使用することができます。</div> | |
| + | <br> | ||
| − | == [[ | + | =====実行例1===== |
| + | <div>切り出したい部分の座標、幅が分かっている場合は[[mrcImageCenterGet]]を使います。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-TomogramSmth.mrc|入力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-TomogramSmth.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-TomogramSmth.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-TomogramSmth.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.00136636 (75, 42, 133)<br> | ||
| + | 0.00292404 (94, 65, 68)<br> | ||
| + | -9.48921e-07<br> | ||
| + | 0.00013513<br> | ||
| + | 8.71152e-08<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド: [[mrcImageCenterGet]] -i Input-TomogramSmth.mrc -o Input-TomogramSub.mrc -Cx 67 -Cy 67 -Cz 67 -Nx 27 -Ny 27 -Nz 27</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-TomogramSub.mrc|出力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-TomogramSub.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-TomogramSub.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-TomogramSub.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.0012017 (5, 9, 13)<br> | ||
| + | 0.00263957 (13, 6, 15)<br> | ||
| + | 2.22923e-05<br> | ||
| + | 0.000388094<br> | ||
| + | 2.76625e-06<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ====2次元画像の切り出し==== | ||
| + | <div> 視野全体ではなく、一部だけ再構成するために傾斜画像から部分的に2次元画像を切り出す場合もあります。視野全体の再構成よりもコストが削減されるので、部分的なデータだけあれば十分な場合はこの手法を用います。試料を傾けながら撮影しているので、画像から切り出す位置や角度を画像によって変える必要があります。切り出すときには[[mrcImageCenterGet]]や[[mrcImageROI]]、[[mrcImageROIs]]などを使用します。切り出し範囲を全て手動で決めるのはかなりの時間を要しますので、基準(0°)の画像での切り出し範囲を手動で決めると残りの切り出し位置を傾斜角度に応じて自動で計算して切り出しを行う方法をとります。</div> | ||
| + | 操作動画: [[:Media:Tomography4-1.mov|(.mov)]] [[:Media:Tomography4-1.mp4|(.mp4)]]<br> | ||
| + | <br> | ||
| + | |||
| + | <div>以下の流れで3次元再構成まで行います。</div> | ||
| + | <pre> | ||
| + | 傾斜画像(2D画像複数)(前処理済) | ||
| + | |||
| + | ↓ 切り出し範囲の設定(Display2: 0°の画像のみ) | ||
| + | |||
| + | 0°の切り出し情報ファイル(ROI情報) | ||
| + | |||
| + | ↓ 各傾斜画像の切り出し範囲を計算する(現在はMakefile内で処理) | ||
| + | |||
| + | 各傾斜画像の切り出し情報 | ||
| + | |||
| + | ↓ 画像の切り出し(mrcImageROIs) | ||
| + | |||
| + | 切り出された複数の画像ファイル(切り出し数 × 傾斜数分) | ||
| + | |||
| + | ↓ 位置合わせ(mrcImageCorrelarion + Makefileの処理) | ||
| + | |||
| + | 位置合わせ済みの切り出し情報(傾斜数分) | ||
| + | |||
| + | ↓ 再度画像の切り出し(mrcImageROIs) (※ 切り出し画像をシフトするのではなく、切り出し位置を再設定して切り出します) | ||
| + | |||
| + | 位置合わせ済みの画像(ROI)ファイル(切り出し数 × 傾斜数分) | ||
| + | |||
| + | ↓ 角度情報ファイルの作成(Makefile内の処理) | ||
| + | |||
| + | 角度情報ファイル(切り出し数分) | ||
| + | |||
| + | ↓ 3次元再構成(mrc2Dto3D) | ||
| + | |||
| + | 3次元画像(切り出し数分) | ||
| + | </pre> | ||
| + | |||
| + | =====実行例1(1軸傾斜のサブトモグラム)===== | ||
| + | <div>[[Media:Input-Tomogram2DSet1.zip|入力ファイル]]の画像(一部)(y軸傾斜: -60° ~ 60°: 2°刻み)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-Tomogram2DSet1.png]]<br> | ||
| + | -60°(p1_001.mrc)<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-Tomogram2DSet1.png]]<br> | ||
| + | 0°(p1_031.mrc)<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-Tomogram2DSet1.png]]<br> | ||
| + | 60°(p1_061.mrc)<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>[[:Media:Makefile-Tomogram4.zip|こちらのMakefile]]を使用します。</div> | ||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make all | ||
| + | </pre> | ||
| + | |||
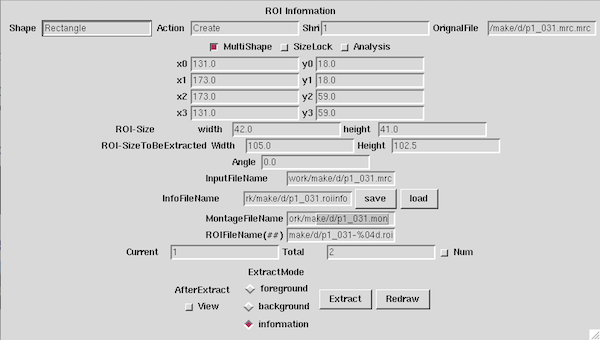
| + | <div>コマンドを入力後に[[Display2]](2Dビューワー)が開きますので、切り出したい部分(複数可)を選択しInformationファイル(.roiinfo)を作成します。</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Tomogram1.png]]</p></td> | ||
| + | <td><p align="Center">[[画像:Tomogram2.png]]</p></td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td><p align="Center">切り出し部分決めてEdit->OKで決定します。</p></td> | ||
| + | <td><p align="Center">複数切り出したいときはROI->MultiROIを選択します。</p> </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Tomogram3.png]]</p></td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>今回はInformationだけ作成すれば、切り出しは自動で行われます。<br> | ||
| + | ROI InformationウィンドウにてInfoFileName右側のsaveボタンを押すとファイルが作成されます。<br> | ||
| + | (またはExtractModeをInformationにしてExtractボタンを押します。)</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>今回出力したInformationファイル</div> | ||
| + | <pre> | ||
| + | p1_031-0000.roi Rect 20 30 60 30 60 70 20 70 | ||
| + | p1_031-0001.roi Rect 15 75 55 75 55 115 15 115 | ||
| + | p1_031-0002.roi Rect 25 110 65 110 65 150 25 150 | ||
| + | p1_031-0003.roi Rect 45 0 85 0 85 40 45 40 | ||
| + | p1_031-0004.roi Rect 60 50 100 50 100 90 60 90 | ||
| + | p1_031-0005.roi Rect 55 80 95 80 95 120 55 120 | ||
| + | p1_031-0006.roi Rect 55 120 95 120 95 160 55 160 | ||
| + | p1_031-0007.roi Rect 85 15 125 15 125 55 85 55 | ||
| + | p1_031-0008.roi Rect 85 51 125 51 125 91 85 91 | ||
| + | p1_031-0009.roi Rect 85 91 125 91 125 131 85 131 | ||
| + | p1_031-0010.roi Rect 93 130 133 130 133 170 93 170 | ||
| + | p1_031-0011.roi Rect 115 25 155 25 155 65 115 65 | ||
| + | p1_031-0012.roi Rect 120 60 160 60 160 100 120 100 | ||
| + | p1_031-0013.roi Rect 123 100 163 100 163 140 123 140 | ||
| + | p1_031-0014.roi Rect 115 140 155 140 155 180 115 180 | ||
| + | p1_031-0015.roi Rect 152 152 192 152 192 192 152 192 | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>1枚の画像について[[Display2]]からInformationファイル(.roiinfo)を作成すると、残りの画像については傾きから切り出す範囲を計算し、自動で切り出しが行われます。</div> | ||
| + | <br> | ||
| + | <div>自動で切り出された画像(縦: 選択範囲毎, 横: ファイル(角度)毎)(.pad)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td></td> | ||
| + | <td>[[画像:Tomogram-Segmentation.png]]</td> | ||
| + | <td></td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>-60°</td> | ||
| + | <td><p align="Center">0°</p></td> | ||
| + | <td>60°</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>切り出し処理を終えた後はそれぞれの画像に対して3次元再構成が行われます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>再構成されたそれぞれの3次元画像(.mrc3d)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Outdata-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Outdata1-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Outdata2-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | =====実行例2(2軸傾斜のサブトモグラム)===== | ||
| + | <div> 2軸で傾斜した画像から切り出し及び再構成を行ってみます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-Tomogram2DSet2.zip|入力ファイル]]の画像(一部)(x軸, y軸傾斜: -60° ~ 60°: 10°刻み)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>x軸傾斜</td> | ||
| + | <td><p align="Center">[[画像:Input-Tomogram2DSet2.png]]<br> | ||
| + | -60°<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-Tomogram2DSet2.png]]<br> | ||
| + | 0°<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-Tomogram2DSet2.png]]<br> | ||
| + | 60°<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>y軸傾斜</td> | ||
| + | <td><p align="Center">[[画像:Input3-Tomogram2DSet2.png]]<br> | ||
| + | -60°<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input4-Tomogram2DSet2.png]]<br> | ||
| + | 0°<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input5-Tomogram2DSet2.png]]<br> | ||
| + | 60°<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>[[:Media:Makefile-Tomogram5.zip|こちらのMakefile]]を使用します。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド</div> | ||
| + | <pre> | ||
| + | make all | ||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>今回はこの領域でROIファイルの切り出しを行います。</div> | ||
| + | <div>[[画像:Tomogram2-Segmanetation.png]]</div> | ||
| + | <div>今回出力したInformationファイル</div> | ||
| + | <pre> | ||
| + | DataA_006-0000.roi Rect 0.722314 137.147614 33.000000 106.000000 49.053597 122.636041 16.775911 153.783654 | ||
| + | DataA_006-0001.roi Rect 15.000000 79.000000 42.000000 79.000000 42.000000 107.000000 15.000000 107.000000 | ||
| + | DataA_006-0002.roi Rect 13.000000 39.000000 58.000000 39.000000 58.000000 64.000000 13.000000 64.000000 | ||
| + | DataA_006-0003.roi Rect 41.000000 129.000000 84.000000 129.000000 84.000000 154.000000 41.000000 154.000000 | ||
| + | DataA_006-0004.roi Rect 51.000000 85.000000 82.000000 85.000000 82.000000 119.000000 51.000000 119.000000 | ||
| + | DataA_006-0005.roi Rect 47.269722 69.494676 78.455043 40.316766 95.000000 58.000000 63.814679 87.177909 | ||
| + | DataA_006-0006.roi Rect 66.000000 4.000000 92.000000 4.000000 92.000000 44.000000 66.000000 44.000000 | ||
| + | DataA_006-0007.roi Rect 77.597890 150.922358 95.484138 132.052220 120.886248 156.129861 103.000000 175.000000 | ||
| + | DataA_006-0008.roi Rect 93.000000 92.000000 115.000000 92.000000 115.000000 132.000000 93.000000 132.000000 | ||
| + | DataA_006-0009.roi Rect 100.000000 51.000000 121.000000 51.000000 121.000000 93.000000 100.000000 93.000000 | ||
| + | DataA_006-0010.roi Rect 98.589377 19.087800 119.760822 10.100593 135.000000 46.000000 113.828555 54.987208 | ||
| + | DataA_006-0011.roi Rect 122.000000 141.000000 146.000000 141.000000 146.000000 184.000000 122.000000 184.000000 | ||
| + | DataA_006-0012.roi Rect 136.883039 95.213292 160.000000 104.000000 144.116961 145.786708 121.000000 137.000000 | ||
| + | DataA_006-0013.roi Rect 127.000000 73.000000 146.061183 60.635990 169.000000 96.000000 149.938817 108.364010 | ||
| + | DataA_006-0014.roi Rect 140.000000 22.000000 177.361289 43.286947 166.470292 62.402025 129.109004 41.115078 | ||
| + | DataA_006-0015.roi Rect 163.000000 152.000000 183.000000 152.000000 183.000000 190.000000 163.000000 190.000000 | ||
| + | |||
| + | </pre> | ||
| + | <br> | ||
| + | |||
| + | <div>自動で切り出された画像(縦: 選択範囲毎, 横: ファイル(角度)毎)(.pad)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Tomogram2-Segmanetation1.png]]<br> | ||
| + | DataA(x軸傾斜)<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Tomogram2-Segmanetation2.png]]<br> | ||
| + | DataB(y軸傾斜)<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div>切り出しサイズがバラバラで分かりにくくなっていますが、いずれの傾斜軸でもROIファイルが自動で切り出されています。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>再構成されたそれぞれの3次元画像(.mrc3d)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Outdata-Tomogram1.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Outdata1-Tomogram1.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Outdata2-Tomogram1.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | == [[トモグラム画像の解釈]] == | ||
| + | |||
| + | |||
| + | === [[サブトモグラム画像の平均化]] === | ||
| + | <div> セグメンテーションによって分割された3次元データ同士が別方向を向いている同じ粒子であるとき、それを平均化することでミッシングエリアを補間し、より精密な3次元像にすることができます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>分割したデータ1</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>[[画像:Input-SubTomogram.png]]</td> | ||
| + | <td>[[画像:Input1-SubTomogram.png]]</td> | ||
| + | <td>[[画像:Input2-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div>分割したデータ2(90°向きが違う)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>[[画像:Input-SubTomogram1.png]]</td> | ||
| + | <td>[[画像:Input1-SubTomogram2.png]]</td> | ||
| + | <td>[[画像:Input2-SubTomogram3.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div>平均したデータ</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>[[画像:Output-SubTomogram1.png]]</td> | ||
| + | <td>[[画像:Output1-SubTomogram2.png]]</td> | ||
| + | <td>[[画像:Output2-SubTomogram3.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>yz平面</td> | ||
| + | <td>zx平面</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | ====実行例1==== | ||
| + | <div>[[Media:Input-Mean-SubTomogram.zip|入力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Input-Mean-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Input1-Mean-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Input2-Mean-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>3次元像を平均化する前に[[mrcImageAutoRotationCorrelation3D]]を使って、向きを合わせます。</div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-TomogramSub.mrc|参照ファイル]](入力ファイルの真ん中のデータを使用)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-TomogramSub.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-TomogramSub.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-TomogramSub.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.0012017 (5, 9, 13)<br> | ||
| + | 0.00263957 (13, 6, 15)<br> | ||
| + | 2.22923e-05<br> | ||
| + | 0.000388094<br> | ||
| + | 2.76625e-06<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>コマンド: [[mrcImageAutoRotationCorrelation3D]] -i c1-1.mrc -r c2-2.mrc -fit f1-1.mrc -EA YOYS -Rot1 0 0 30 -Rot2 0 330 30 -Rot3 0 330 30 -Xrange 0 0 -Yrange 0 0 -Zrange 0 0 </div> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-Fit-SubTomogram.zip|補正後のデータ]](-fitの出力ファイル)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Input-Fit-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Input1-Fit-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Input2-Fit-SubTomogram.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>補正ファイルに対し、[[mrcImageAverage]]にて平均化を行います。</div> | ||
| + | <div>出力ファイル</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Outdata-TomogramSub.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata1-TomogramSub.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata2-TomogramSub.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-0.000536652 (6, 13, 12)<br> | ||
| + | 0.00177258 (13, 17, 13)<br> | ||
| + | 3.22171e-05<br> | ||
| + | 0.000228739<br> | ||
| + | 1.6304e-06<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <div>平均化することにより3次元像の質(特にyz平面)が良くなりました。</div> | ||
| + | <br> | ||
| + | |||
| + | ====実行例2==== | ||
| + | <div>[[Media:Outdata-Tomogram.zip|入力ファイル]]</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Outdata-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Outdata1-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Outdata2-Tomogram.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>[[Media:Input-TomogramSub1.mrc|参照ファイル]](入力ファイルの先頭のデータを使用)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Input-TomogramSub1.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input1-TomogramSub1.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Input2-TomogramSub1.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-5.47817 (34, 19, 20)<br> | ||
| + | 16.0715 (31, 22, 19)<br> | ||
| + | 0.142234<br> | ||
| + | 1.22547<br> | ||
| + | 0.0048441<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
| + | <div>同様にまず向きを合わせます。</div> | ||
| + | <div>コマンド: [[mrcImageAutoRotationCorrelation3D]] -i p1-0001.mrc3d -r Target.mrc3dref -fit p1-0001.3dfit -EA XEYR -Rot1 0 355 5 -Rot2 0 355 5 -Rot3 0 0 30 -M 18</div> | ||
| + | <br> | ||
| + | <div>[[Media:Input-Fit-SubTomogram1.zip|補正後のデータ]](-fitの出力ファイル)</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td>xy平面</td> | ||
| + | <td>[[画像:Input-Fit-SubTomogram1.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>yz平面</td> | ||
| + | <td>[[画像:Input1-Fit-SubTomogram1.png]]</td> | ||
| + | </tr> | ||
| + | <tr> | ||
| + | <td>zx平面</td> | ||
| + | <td>[[画像:Input2-Fit-SubTomogram1.png]]</td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
| + | |||
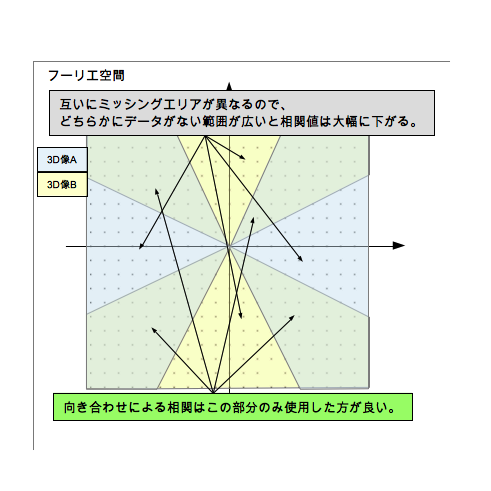
| + | <div>参照ファイルに対して向きが合っているものと合っていないものがあります。<br> | ||
| + | これはそれぞれのサブトモグラムの3次元像にてミッシングエリアが異なるので、どちらかにデータがない角度では相関値が大幅に下がってしまうためです。</div> | ||
| + | <div>[[画像:Fig-SubTomogram.png]]</div> | ||
| + | <br> | ||
| + | |||
| + | <div>補正ファイルに対し、[[mrcImageAverage]]にて平均化を行います。</div> | ||
| + | <div>出力ファイル</div> | ||
| + | <table> | ||
| + | <tr> | ||
| + | <td><p align="Center">[[画像:Outdata-TomogramSub1.png]]<br> | ||
| + | xy平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata1-TomogramSub1.png]]<br> | ||
| + | yz平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="Center">[[画像:Outdata2-TomogramSub1.png]]<br> | ||
| + | zx平面<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">最小<br> | ||
| + | 最大<br> | ||
| + | 平均値<br> | ||
| + | 標準偏差<br> | ||
| + | 標準誤差<br></p> | ||
| + | </td> | ||
| + | <td><p align="left">-2.32263 (22, 29, 20)<br> | ||
| + | 5.20816 (19, 24, 22)<br> | ||
| + | 0.0844992<br> | ||
| + | 0.49404<br> | ||
| + | 0.00195286<br></p> | ||
| + | </td> | ||
| + | </tr> | ||
| + | </table> | ||
| + | <br> | ||
2014年10月10日 (金) 08:07時点における最新版
電子線トモグラフィーとは、電子顕微鏡を用いた3次元再構成法の一つで、同一視野を様々な方向からの投影された電子顕微鏡像をコンピュータの中で三次元像に再構成し、コンピュータを使って断層像(トモグラム)を作成する手法です。
下記にその手順を順に述べていきます。
目次
連続傾斜像の撮影
 1軸傾斜 (中央が0°の画像) |
 2軸傾斜(中央が0°の画像)(上の画像より90°回転した向きになっている) |
画像の補正
傾斜画像では、視野全体がアンダーフォーカスとなるように、通常の電子顕微鏡撮影よりも大きなデフォカース値をとる場合が多いです。その場合、LaB6などの電子銃では第一トーンリングより外側の情報がほとんど無いために、CTF補正等は必要ありませんが、電界放出銃を利用した場合には、場合によっては間違った情報を与える場合があるので注意が必要です。
ラフ・アラインメント
傾斜画像の中心付近の画像の相関から、それぞれの傾斜画像の大まかな位置を合わせます。
前処理(窓関数)
# For Windowing WIN_X=0.2 WIN_X_MAX=0.2 WIN_Y=0.1 WIN_Y_MAX=0.1 WIN_MODE=18
make Windowing
位置合わせ
例. 2°刻みで撮影した画像の場合
2°画像の位置を0°画像の位置に合わせる
4°画像の位置を位置補正後の2°画像の位置に合わせる
6°画像の位置を位置補正後の4°画像の位置に合わせる
.
.
mrcImageCorrelationを使用した場合
実行例1
make CorFit1
ファイン・アラインメント
実行例1(傾斜軸の調整)
# RotMode ROTMODE=ZOYS # Rot1 ROT1MIN=10 ROT1MAX=10 ROT1D=10 # Rot2 ROT2MIN=-60 ROT2MAX=60 ROT2D=2 # Rot3 ROT3MIN=0 ROT3MAX=0 ROT3D=30 ### For mrcImageMove SHIFT2MAX=10 SHIFT3MAX=0 ### For mrcImageTiltAxisSearch TILTMIN=0 TILTMAX=20 TILTN=10 TILTITER=1 TILTSCALE=5
make TiltFit
9.895
| 補正前 | ||
 |
 |
 |
| 補正後 | ||
 |
 |
 |
| xy平面 | yz平面 | zx平面 |
実行例2(傾斜軸の繰り返し調整)
# For mrcImageTiltAxisSearch IN_TILT_EXT=roi # RotMode ROTMODE=ZEYR # Rot1 ROT1MIN=1 ROT1MAX=1 ROT1D=1 # Rot2 ROT2MIN=-60 ROT2MAX=60 ROT2D=10 # Rot3 ROT3MIN=0 ROT3MAX=0 ROT3D=10 ### For mrcImageTiltAxisSearch TILTMIN=-10 TILTMAX=10 TILTN=10 TILTITER=100 TILTSCALE=5
make TiltFit
0.084 0.161 0.230 0.294 0.345 -中略- 0.701 0.700 0.685 0.706 0.701
3次元再構成
最小 最大 |
0 (0, 0, 0) 4 (31, 26, 26) |
mrc2Dto3Dで実行
実行例1(1軸傾斜での再構成)
# For Reconstruction IN_3D_EXT=fit # RotMode ROTMODE=YOYS # Rot1 ROT1MIN=-60 ROT1MAX=60 ROT1D=2 # Rot2 ROT2MIN=0 ROT2MAX=0 # Rot3 ROT3MIN=0 ROT3MAX=0
make 3DList make Input.3d
最小 最大 |
-0.00437076 (39, 34, 36) 0.00799233 (37, 34, 36) |
実行例2(2軸傾斜での再構成)
make all
今回出力したInformationファイル
DataA_006.mrcsmth-0000.roi Rect 0.000000 0.000000 63.000000 0.000000 63.000000 63.000000 0.000000 63.000000
最小 最大 |
-9.32199 (29, 37, 34) 21.995 (40, 35, 32) |
実行例3(Doubleを使用した2軸傾斜での再構成)
.roilst.mrc3d: # mrc2Dto3D -I $*.roilst -o $*.mrc3d -single 0 -InterpolationMode 2 -m 1 mrc2Dto3D -I $*.roilst -o $*.mrc3d -Double -InterpolationMode 2 -m 1
最小 最大 |
-10360.9 (41, 24, 0) 8132.05 (40, 35, 31) |
ラドン変換を使った3次元再構成で実行
位置合わせ済みの2Dリスト
↓mrcImageSinogramCreate
シノグラムリスト
↓mrcRadon2Dto3D
3Dラドンファイル
↓mrcImageInverseRadonTransform
実行例1
make Radon3D
| xy平面 | yz平面 | zx平面 |
 |
 |
 |
最小 最大 |
1.84923e+06 (0, 59, 28) 1.17991e+07 (34, 31, 30) |
実行例2
### RadonTransform RBP_MODE=4 RBP_OPTION=-Rmin 0.05 -Rmax 0.1
make Radon3D
| xy平面 | yz平面 | zx平面 |
 |
 |
 |
最小 最大 |
-344789 (25, 25, 0) 631546 (37, 34, 28) |
電子線トモグラフィー画像のもつ問題点
ミッシングエリア
最小 最大 |
0 (0, 0, 0) 2 (29, 29, 14) |
TILTAXISNUMBER=1 # Single: 1 Double: 2
make Target.ini2d make TestData2DSet make all
最小 最大 |
-0.00330818 (52, 36, 32) 0.00425516 (13, 37, 32) |
TILTAXISNUMBER=2 # Single: 1 Double: 2
make Target.ini2d1 make TestData2DSetDouble make all
最小 最大 |
-0.00248567 (12, 38, 32) 0.00344027 (13, 37, 32) |
画像の位置、フォーカスの問題
平行移動の補正
軸の決定
トモグラフに使われる画像処理
平滑化
実行例1
最小 最大 |
-0.00268221 (76, 92, 66) 0.00642324 (89, 42, 71) |
最小 最大 |
-0.00136636 (75, 42, 133) 0.00292404 (94, 65, 68) |
セグメンテーション
トモグラムは多様な構造を含むため、3次元画像から興味あるセグメントを切り出すなどの作業が必要です。そのための支援ソフトウェアが必要です。場合によっては2次元画像から切り出すこともあります。
3次元画像の切り出し
実行例1
最小 最大 |
-0.00136636 (75, 42, 133) 0.00292404 (94, 65, 68) |
最小 最大 |
-0.0012017 (5, 9, 13) 0.00263957 (13, 6, 15) |
2次元画像の切り出し
傾斜画像(2D画像複数)(前処理済) ↓ 切り出し範囲の設定(Display2: 0°の画像のみ) 0°の切り出し情報ファイル(ROI情報) ↓ 各傾斜画像の切り出し範囲を計算する(現在はMakefile内で処理) 各傾斜画像の切り出し情報 ↓ 画像の切り出し(mrcImageROIs) 切り出された複数の画像ファイル(切り出し数 × 傾斜数分) ↓ 位置合わせ(mrcImageCorrelarion + Makefileの処理) 位置合わせ済みの切り出し情報(傾斜数分) ↓ 再度画像の切り出し(mrcImageROIs) (※ 切り出し画像をシフトするのではなく、切り出し位置を再設定して切り出します) 位置合わせ済みの画像(ROI)ファイル(切り出し数 × 傾斜数分) ↓ 角度情報ファイルの作成(Makefile内の処理) 角度情報ファイル(切り出し数分) ↓ 3次元再構成(mrc2Dto3D) 3次元画像(切り出し数分)
実行例1(1軸傾斜のサブトモグラム)
make all
切り出し部分決めてEdit->OKで決定します。 |
複数切り出したいときはROI->MultiROIを選択します。 |
| 今回はInformationだけ作成すれば、切り出しは自動で行われます。 ROI InformationウィンドウにてInfoFileName右側のsaveボタンを押すとファイルが作成されます。 |
p1_031-0000.roi Rect 20 30 60 30 60 70 20 70 p1_031-0001.roi Rect 15 75 55 75 55 115 15 115 p1_031-0002.roi Rect 25 110 65 110 65 150 25 150 p1_031-0003.roi Rect 45 0 85 0 85 40 45 40 p1_031-0004.roi Rect 60 50 100 50 100 90 60 90 p1_031-0005.roi Rect 55 80 95 80 95 120 55 120 p1_031-0006.roi Rect 55 120 95 120 95 160 55 160 p1_031-0007.roi Rect 85 15 125 15 125 55 85 55 p1_031-0008.roi Rect 85 51 125 51 125 91 85 91 p1_031-0009.roi Rect 85 91 125 91 125 131 85 131 p1_031-0010.roi Rect 93 130 133 130 133 170 93 170 p1_031-0011.roi Rect 115 25 155 25 155 65 115 65 p1_031-0012.roi Rect 120 60 160 60 160 100 120 100 p1_031-0013.roi Rect 123 100 163 100 163 140 123 140 p1_031-0014.roi Rect 115 140 155 140 155 180 115 180 p1_031-0015.roi Rect 152 152 192 152 192 192 152 192
 |
||
| -60° | 0° |
60° |
| xy平面 | |
| yz平面 | |
| zx平面 |
実行例2(2軸傾斜のサブトモグラム)
| x軸傾斜 | |||
| y軸傾斜 |
make all
DataA_006-0000.roi Rect 0.722314 137.147614 33.000000 106.000000 49.053597 122.636041 16.775911 153.783654 DataA_006-0001.roi Rect 15.000000 79.000000 42.000000 79.000000 42.000000 107.000000 15.000000 107.000000 DataA_006-0002.roi Rect 13.000000 39.000000 58.000000 39.000000 58.000000 64.000000 13.000000 64.000000 DataA_006-0003.roi Rect 41.000000 129.000000 84.000000 129.000000 84.000000 154.000000 41.000000 154.000000 DataA_006-0004.roi Rect 51.000000 85.000000 82.000000 85.000000 82.000000 119.000000 51.000000 119.000000 DataA_006-0005.roi Rect 47.269722 69.494676 78.455043 40.316766 95.000000 58.000000 63.814679 87.177909 DataA_006-0006.roi Rect 66.000000 4.000000 92.000000 4.000000 92.000000 44.000000 66.000000 44.000000 DataA_006-0007.roi Rect 77.597890 150.922358 95.484138 132.052220 120.886248 156.129861 103.000000 175.000000 DataA_006-0008.roi Rect 93.000000 92.000000 115.000000 92.000000 115.000000 132.000000 93.000000 132.000000 DataA_006-0009.roi Rect 100.000000 51.000000 121.000000 51.000000 121.000000 93.000000 100.000000 93.000000 DataA_006-0010.roi Rect 98.589377 19.087800 119.760822 10.100593 135.000000 46.000000 113.828555 54.987208 DataA_006-0011.roi Rect 122.000000 141.000000 146.000000 141.000000 146.000000 184.000000 122.000000 184.000000 DataA_006-0012.roi Rect 136.883039 95.213292 160.000000 104.000000 144.116961 145.786708 121.000000 137.000000 DataA_006-0013.roi Rect 127.000000 73.000000 146.061183 60.635990 169.000000 96.000000 149.938817 108.364010 DataA_006-0014.roi Rect 140.000000 22.000000 177.361289 43.286947 166.470292 62.402025 129.109004 41.115078 DataA_006-0015.roi Rect 163.000000 152.000000 183.000000 152.000000 183.000000 190.000000 163.000000 190.000000
| xy平面 | |
| yz平面 | |
| zx平面 |
トモグラム画像の解釈
サブトモグラム画像の平均化
 |
 |
 |
 |
 |
 |
 |
 |
 |
| xy平面 | yz平面 | zx平面 |
実行例1
| xy平面 | |
| yz平面 | |
| zx平面 |
最小 最大 |
-0.0012017 (5, 9, 13) 0.00263957 (13, 6, 15) |
| xy平面 | |
| yz平面 | |
| zx平面 |
最小 最大 |
-0.000536652 (6, 13, 12) 0.00177258 (13, 17, 13) |
実行例2
| xy平面 | |
| yz平面 | |
| zx平面 |
最小 最大 |
-5.47817 (34, 19, 20) 16.0715 (31, 22, 19) |
| xy平面 | |
| yz平面 | |
| zx平面 |
これはそれぞれのサブトモグラムの3次元像にてミッシングエリアが異なるので、どちらかにデータがない角度では相関値が大幅に下がってしまうためです。
最小 最大 |
-2.32263 (22, 29, 20) 5.20816 (19, 24, 22) |